Pflanzen unterscheiden sich von Tieren dadurch, dass sie Photosynthese betreiben können. Sie tun das in spezialisierten „Mini-Organen“ (Biologen sprechen von Organellen), den Chloroplasten. Chloroplasten produzieren mit Hilfe von Sonnenlicht Zucker, der wiederum in anderen Organellen – den Mitochondrien – zur Energiegewinnung genutzt wird.
Sowohl Chloroplasten als auch Mitochondrien verfügen über ein eigenes Erbgut. Und bei beiden enthält dieses Genom jede Menge Fehler. „Zumindest ist das bei fast allen Landpflanzen so“, erklärt Dr. Mareike Schallenberg-Rüdinger. Die Wissenschaftlerin leitet an der Universität Bonn in der Abteilung Molekulare Evolution von Prof. Volker Knoop eine Nachwuchsgruppe. „Sie müssen diese Fehler korrigieren, damit ihre Energieversorgung nicht zusammenbricht.“
Tatsächlich machen die Landpflanzen das auch, und zwar auf einem denkbar komplizierten Weg: Sie verbessern nicht etwa die Fehler im Genom selbst. Stattdessen berichtigen sie die Abschriften, die die Zelle von diesen Bauanleitungen anfertigt und mit deren Hilfe sie dann zum Beispiel bestimmte Enzyme herstellt. Anstatt also gleich das Original zu korrigieren, bügelt sie die Inkorrektheiten erst nachträglich bei den Kopien aus.
Funktionsfähig trotz 400 Millionen Jahren Evolutionsgeschichte
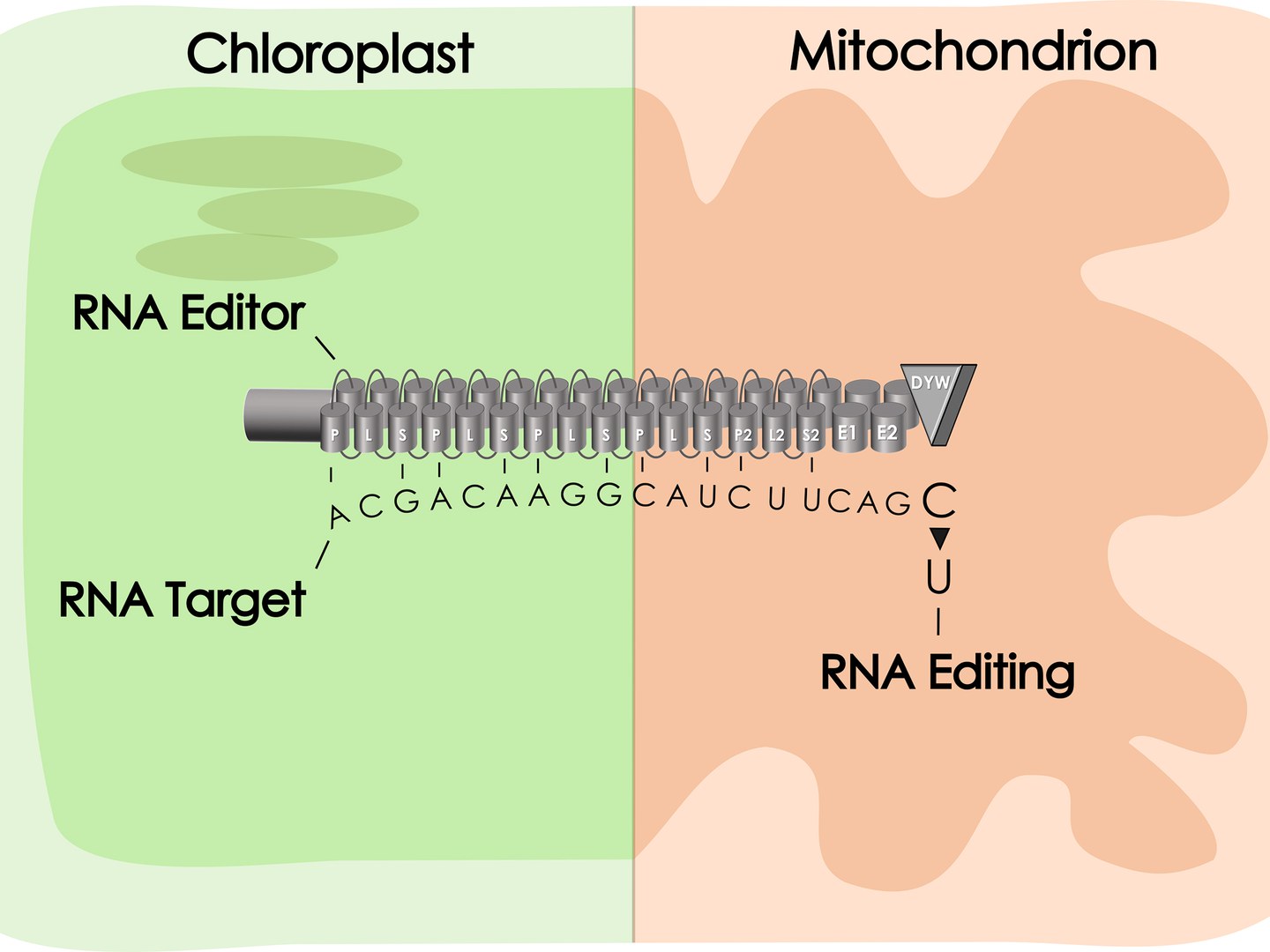
Verantwortlich dafür sind molekulare Korrekturleser, die so genannten PPR-Proteine. Die meisten sind Spezialisten für nur einen ganz bestimmten Fehler in den vielen Gen-Abschriften, die die Zelle rund um die Uhr herstellt. Diese Fehler entstehen, wenn im Laufe der Evolution ein bestimmter chemischer Baustein der DNA (wenn man so will, ein Buchstabe in der genetischen Bauanleitung) gegen einen anderen ausgetauscht wird. Wenn die PPR-Proteine einen solchen Austausch finden, wandeln sie den falschen Buchstaben in der DNA-Abschrift (den Baustein Cytidin, abgekürzt C) in die richtige Version (Uridin, abgekürzt U) um.
„Wir haben nun ein Gen für ein PPR-Protein aus dem Laubmoos Physcomitrium patens genommen und in eine Blütenpflanze verfrachtet, die Ackerschmalwand Arabidopsis thaliana“, erklärt Schallenberg-Rüdinger. „Das Protein erkannte und korrigierte dort dann den gleichen Fehler, für den es auch im Moos verantwortlich war.“ Das ist erstaunlich, liegen doch zwischen Physcomitrium und Arabidopsis mehr als 400 Millionen Jahre Evolutionsgeschichte. Daher können die PPR Proteine sich auch in ihrem Aufbau deutlich unterscheiden.
So gibt es etwa in der Ackerschmalwand PPR-Proteine, die zwar Fehler erkennen können, zu ihrer Korrektur aber noch ein separates „Tipp-Ex“-Enzym benötigen. Die PPR-Proteine des Laubmooses Physcomitrium übernehmen dagegen beide Aufgaben zugleich. „In diesen Fällen funktioniert daher zwar der Transfer vom Moos in die Ackerschmalwand; umgekehrt bleibt das Ackerschmalwand-Gen im Moos dagegen funktionslos“, erklärt Bastian Oldenkott, Doktorand und Erstautor der Studie. Etwas früher als Arabidopsis trat in der Evolution die Macadamia-Nuss auf. Ihr untersuchtes PPR-Protein ist dem aus Physcomitrium ähnlicher. In das Moos eingebracht, verrichtet es dort daher anstandslos seinen Dienst.
Die Studie eröffnet möglicherweise einen neuen Weg, das Erbgut von Chloroplasten und Mitochondrien zu modifizieren. „Insbesondere für pflanzliche Mitochondrien ist das bislang noch gar nicht möglich“, betont Schallenberg-Rüdinger. Durch die Nutzung spezieller „Designer“-PPR-Gene könnte man zum Beispiel gezielt bestimmte Genom-Abschriften unbrauchbar machen und testen, wie sich das auf die Pflanze auswirkt. Eventuell ergeben sich daraus mittelfristig auch neue Erkenntnisse für die Züchtung besonders ertragreicher Hochleistungs-Sorten. Zunächst aber erhoffen sich die Wissenschaftler Einblicke in das komplexe Zusammenspiel der Gene bei der Funktion von Chloroplasten und Mitochondrien.
Dass dieser Ansatz tatsächlich funktionieren kann, belegen die Arbeiten, die die Koautoren Prof. Hans-Peter Braun und Dr. Jennifer Senkler von der Universität Hannover durchgeführt haben. Sie konnten aufklären, wofür das PPR-Protein aus dem Moos nötig ist: Wenn es fehlt, kann die Pflanze die Maschinerie für die so genannte Atmungskette in den Mitochondrien nicht mehr korrekt zusammenbauen, die der Energiegewinnung dient. Die Arbeiten in der Ackerschmalwand erfolgten in Zusammenarbeit mit Matthias Burger (Universität Ulm) und Prof. Mizuki Takenaka (Universität Kyoto), ein schönes Beispiel für eine erfolgreiche internationale Kooperation.
Publikation: Bastian Oldenkott, Matthias Burger, Anke-Christiane Hein, Anja Jörg, Jennifer Senkler, Hans-Peter Braun, Volker Knoop, Mizuki Takenaka and Mareike Schallenberg-Rüdinger: One C-to-U RNA editing site and two independently evolved editing factors: testing reciprocal complementation with DYW-type PPR proteins from the moss Physcomitrium (Physcomitrella) patens and the flowering plants Macadamia integrifolia and Arabidopsis thaliana; The Plant Cell; DOI: https://doi.org/10.1105/tpc.20.00311
Kontakt:
Dr. Mareike Schallenberg-Rüdinger
Institut für Zelluläre und Molekulare Botanik
Abteilung Molekulare Evolution
Universität Bonn
Tel. +49-(0)228-736464
E-mail: mrueding@uni-bonn.de